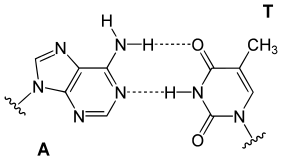
Párování bází
Párování bází je označení pro způsob, jímž jsou nukleové báze (ať v DNA či v RNA) navzájem pospojovány pomocí vodíkových můstků. V typickém případě se párování bází odehrává na základě základních watson-crickovských pravidel komplementarity, tzn. báze adenin (A) páruje s thyminem (T) [či s uracilem v dsRNA] a báze guanin (G) páruje s cytosinem.[1] Existují však i alternativní možnosti párování, které umožňují vznik některých méně obvyklých situací.
Pro komplementární pár bází (base pair) se používá zkratka bp.[1]
Watson-crickovské párování
[editovat | editovat zdroj]Dvěma základními páry v typické dvouvláknové DNA je AT pár (adenin + thymin) a GC pár (guanin + cytosin), v dvouvláknové RNA se vyskytuje GC pár rovněž, ale druhým základním párem je AU pár (adenin+uracil). Pro tyto komplementární páry platí, že jedna z nukleových bází je vždy purin (A či G), druhá je pyrimidin (C, T, U).[1] Jakékoliv jiné kombinace nukleových bází by silně deformovaly dvoušroubovici B-DNA a proto se v živých organismech téměř nevyskytují.[2]
V GC páru jsou mezi guaninem a cytosinem tři vodíkové můstky, zatímco v AT páru jsou pouze dva. V učebnicích se běžně uvádí, že přítomnost tří vodíkových vazeb mezi G a C je důvodem vyšší stability oblastí DNA bohatých na GC páry.[3] Ve skutečnosti jsou pravou příčinou tohoto jevu silné patrové interakce mezi nad sebou umístěným guaninovou a cytosinovou nukleovou bází.[4]
Chargaffova pravidla říkají, že v DNA je stejný počet adeninových a thyminových zbytků (A = T), to samé platí pro guanin s cytosinem (G = C). To však nic neříká o tom, v jakém poměru jsou GC a AT páry v molekule DNA. Ve skutečnosti se tzv. obsah GC (GC content), tedy zastoupení GC párů v DNA, pohybuje u bakterií od 25 do 75 %, u savců v rozmezí 39-46 %.[2]
Alternativní párování bází
[editovat | editovat zdroj]
Existuje celá řada dalších možností, jak pomocí vodíkových můstků spárovat báze, neboť atomů schopných podílet se na vzniku vodíkových vazeb je na molekulách purinů i pyrimidinů celá řada. Samostatnou kapitolou je tzv. hoogsteenovské párování pojmenované podle Karsta Hoogsteena, který je v 60. letech 20. století jako první popsal.[5] Co se týče vazeb mezi adeninem a thyminem, hoogsteenovské páry vznikají buď mezi NH2 skupinou adeninu a ketoskupinou thyminu, nebo mezi N7 dusíkem adeninu a vodíkem na C1 thyminu. Podobně mezi guaninem a cytosinem může vznikat alternativní párování mezi ketoskupinou na šesté pozici guaninu a aminoskupinou na čtvrtém uhlíku cytosinu, případně mezi dusíkem na sedmé pozici guaninu a protonovaným dusíkem na pozici N1 cytosinu.[1] Hoogsteenovské párování umožňuje vznik tzv. trojvláknové DNA (tripl-helixu). Mezi čtyřmi do čtverce uspořádanými guaniny dokonce může vzniknout tetraplex, tzv. G-kvartet.[5]
Jinou možností je tzv. wobble párování, které umožňuje úsporné rozeznávání kodonů pomocí tRNA molekul. Při wobble párování může například guanin vytvářet vazbu s uracilem; někdy je rekrutován inosin, jenž má velmi obecné vazebné schopnosti a je schopen vázat se na C, A a U.[6]
Nepřirozené páry bází
[editovat | editovat zdroj]Vědcům se podařilo syntetizovat již mnoho kandidátů na nepřirozené nukleové báze, jen naprostá menšina z nich je však skutečně replikovatelná DNA polymerázami a ještě menší počet umožňuje transkripci do RNA. Pouze u jediného umělého páru nukleových bází byla dosud (r. 2017) prokázána in vivo funkční ekvivalence s přirozenými páry (cytosin-guanin, adenin-thymin).
V r. 1989 se švýcarskému biochemikovi Stevenu Bennerovi a jeho týmu podařilo implementovat do struktury DNA modifikované nukleosidy iso-cytidin a iso-guanosin párující se vodíkovými můstky odlišně od C-G. Nové úseky byly in vitro schopné replikace a transkripce do RNA (přiřazování komplementárních deoxyribonukleosidů i ribonukleosidů).[7] V roce 1990 publikoval objev dalších pozměněných nukleosidů, a sice uměle vytvořeného „κ“ (chemicky 3-β-D-ribofuranosyl-(2,6-diaminopyrimidin)), párujícího se buďto s přirozeným xanthosinem (X) (má však nestálý deoxyribonukleotid) nebo uměle vytvořeným „π“ (chemicky 3-β-D-ribofuranosyl-(1-methyl-pyrazolo[4,3-d]pyrimidin-5,7(4H,6H)-dion)).[8]
V r. 2002 vyvinul japonský biochemik se svým týmem další nepřirozený pár nukleových bází založených na purinu a pyridinu, fungující in vitro při transkripci a translaci, a sice „s“ (chemicky 2-amino-8-(2-thienyl)purin) a „y“ (chemicky pyridin-2-on).[9] V roce 2006 pak vytvořili další takový pár, „Ds“ (chemicky 7-(2-thienyl)imidazo[4,5-b]pyridin) a „Pa“ (chemicky pyrrol-2-karbaldehyd)[10] a v r. 2009 objevili, že vhodnější chování má pár „Ds“ s nově vytvořenou bází „Px“ (chemicky 4-[3-(6-aminohexanamido)-1-propynyl]-2-nitropyrrol).[11]
Skupina amerických vědců vedených Floydem Romesbergem v r. 2008 vytvořila další dvojici párujících se deoxynukleosidů „d5SICS“ (chemicky 2-((2R,4R,5R)-tetrahydro-4-hydroxy-5-(hydroxymethyl)furan-2-yl)-6-methylisochinolin-1(2H)-thion; v popularizačních článcích označovaný jako „Y“[12]) a „dNaM“ (chemicky (1R)-1,4-anhydro-2-deoxy-1-(3-methoxy-2-naftyl)-D-erythro-pentitol; v popularizačních článcích označovaný jako „X“[12] – pozor, nejedná se o xanthosin). Ty již nejsou odvozeny z purinu a pyrimidinu, ale obě obsahují dva kondenzované aromatické cykly. V r. 2012 tým vedený Denisem Malyshevem publikoval funkčnost těchto bází při replikaci in vitro,[13] v r. 2014 pak úspěšné uplatnění in vivo. Vědci přidali do buňky bakterie Escherichia coli plazmid s novými bázemi. Bakterie s plazmidem se rozmnožovaly, jako by byly úplně obyčejné. Uměle syntetizované báze, nutné pro toto množení, byly dodávány z vnějšího prostředí (jejich syntézu buňka neumí) pomocí přenosového aparátu vypůjčeného z řas – gen pro jeho tvorbu byl vložen do genomu bakterie. Nový pár se tak ukázal plně funkčně ekvivalentní přirozeným párům nukleových bází.[14][15] Díky dalšímu výzkumu se podařilo vyvinout nový transportér syntetických bází přes membránu a po chemické optimalizaci umělého páru bází se podařilo v roce 2016 udržet polosyntetický genom bakterie Escherichia coli životaschopný a stabilní, tj. schopný přetrvat minimálně 60 buněčných dělení.[16][17][18][12]
V roce 2015 publikovaly dva týmy syntetických biologů výsledky prací na rozšíření genetické abecedy o další pár bází – „Z“ (chemicky 6-amino-5-nitro-2(1H)-pyridon) a „P“ (chemicky 2-aminoimidazo[1,2-a]-1,3,5-triazin-4(8H)on) a průkazu in vivo jejich rovnocennosti a kombinovatelnosti s přirozenými páry bází v řetězci DNA.[19][20] Pokračující výzkumné práce vyústily ve vytvoření tzv. „hachimoji“ DNA a RNA (z japonských slov hachi – osm a moji – písmeno), obsahujících 8 různých bází vzájemně se párujících tak, že zachovávají geometrické poměry přirozené DNA (2 páry bází jsou přitom přirozené, 2 páry umělé: výše zmíněný pár Z···P a nový pár S···B, kde S je methylcytosin, B izoguanin) a hachimoji DNA je přitom schopna jednoznačného přepisu do hachimoji RNA (v níž S je izocytosin). Objev těchto uměle rozšířených nukleových kyselin byl publikován v r. 2019.[21][22]


Chemická struktura nukleotidů je:[23]
- u hachimoji DNA (vedle přirozených A, T, C, G):
- dS (z deoxyS): 3-methyl-6-amino-5-(1'-β-D-2'-deoxyribofuranosyl)-pyrimidin-2-on
- dB: 6-amino-9-(1'-β-D-2'-deoxyribofuranosyl)-4-hydroxy-5-(hydroxymethyl)-oxolan-2-yl]-1H-purin-2-on
- dZ: 6-amino-3-(1'-β-D-2'-deoxyribofuranosyl)-5-nitro-1H-pyridin-2-on
- dP: 2-amino-8-(1'-β-D-2'-deoxyribofuranosyl)-imidazo-[1,2a]-1,3,5-triazin-[8H]-4-on
- u hachimoji RNA (vedle přirozených A, U, C, G):
- S (též rS): 2-amino-1-(1'-β-D-ribofuranosyl)-4(1H)-pyrimidinon
- B: 6-amino-9-(1'-β-D-ribofuranosyl)-4-hydroxy-5-(hydroxymethyl)-oxolan-2-yl]-1H-purin-2-on
- Z: 6-amino-3-(1'-β-D-ribofuranosyl)-5-nitro-1H-pyridin-2-on
- P: 2-amino-8-(1'-β-D-ribofuranosyl)-imidazo-[1,2a]-1,3,5-triazin-[8H]-4-on
Reference
[editovat | editovat zdroj]- ↑ a b c d Oxford dictionary of biochemistry and molecular biology; revised edition. Příprava vydání R. Cammack et al. New York: Oxford university press, 2006. ISBN 0-19-852917-1.
- ↑ a b VOET, Donald; VOET, Judith. Biochemie. 1.. vyd. Praha: Victoria Publishing, 1995. ISBN 80-85605-44-9.
- ↑ Robert K. Murray; Daryl K. Granner; Joe C. Davis; Peter A. Mayes; Victor W. Rodwell. Harper’s Illustrated Biochemistry; twenty-sixth edition. [s.l.]: [s.n.], 2003. ISBN 0-07-138901-6.
- ↑ YAKOVCHUK, P.; PROTOZANOVA, E.; FRANK-KAMENETSKII, M. D. Base-stacking and base-pairing contributions into thermal stability of the DNA double helix. Nucleic Acids Res.. 2006, roč. 34, čís. 2, s. 564–74. Dostupné online. ISSN 1362-4962.
- ↑ a b NELSON, David L.; COX, Michael M. Lehninger principles of biochemistry. 5. vyd. New York: W. H. Freeman and Company, 2008. Dostupné online. ISBN 978-0-7167-7108-1.
- ↑ LODISH, Harvey, et al.. Molecular Cell Biology. New York: W.H. Freedman and Company, 2004. Dostupné online. ISBN 0-7167-4366-3.
- ↑ SWITZER, Christopher; MORONEY, Simon E.; BENNER, Steven A. Enzymatic incorporation of a new base pair into DNA and RNA. S. 8322–8323. Journal of the American Chemical Society [online]. Říjen 1989. Svazek 111, čís. 21, s. 8322–8323. Dostupné online. ISSN 1520-5126. DOI 10.1021/ja00203a067. (anglicky)
- ↑ PICCIRILLI, Joseph A.; KRAUCH, Tilman; MORONEY, Simon E., BENNER, Steven A. Enzymatic incorporation of a new base pair into DNA and RNA extends the genetic alphabet. S. 33–37. Nature [online]. 4. leden 1990. Svazek 343, čís. 6253, s. 33–37. Dostupné online. ISSN 1476-4687. DOI 10.1038/343033a0. PMID 1688644. (anglicky)
- ↑ HIRAO, Ichiro, a kol. An unnatural base pair for incorporating amino acid analogs into proteins. S. 177–182. Nature Biotechnology [online]. 2002. Svazek 20, čís. 2, s. 177–182. Dostupné online. ISSN 1546-1696. DOI 10.1038/nbt0202-177. PMID 11821864. (anglicky)
- ↑ HIRAO, Ichiro, a kol. An unnatural hydrophobic base pair system: site-specific incorporation of nucleotide analogs into DNA and RNA. S. 729–735. Nature Methods [online]. 23. srpen 2006. Svazek 3, čís. 9, s. 729–735. Dostupné online. ISSN 1548-7105. DOI 10.1038/nmeth915. PMID 16929319. (anglicky)
- ↑ KIMOTO, Michiko, a kol. Generation of high-affinity DNA aptamers using an expanded genetic alphabet. S. 453–457. Nature Biotechnology [online]. 7. duben 2013. Svazek 31, čís. 5, s. 453–457. Dostupné online. ISSN 1548-7105. DOI 10.1038/nbt.2556. PMID 23563318. (anglicky)
- ↑ a b c PAZDERA, Josef. První stabilní polosyntetický organismus. OSEL.cz [online]. 29. leden 2017 [cit. 2017-01-31]. Dostupné online.
- ↑ MALYSHEV, Denis A., a kol. Efficient and sequence-independent replication of DNA containing a third base pair establishes a functional six-letter genetic alphabet. S. 12005–12010. Proceedings of the National Academy of Sciences USA (PNAS) [online]. 24. červenec 2012. Svazek 109, čís. 30, s. 12005–12010. Dostupné online. ISSN 1091-6490. DOI 10.1073/pnas.1205176109. PMID 22773812. (anglicky)
- ↑ MALYSHEV, Denis A., a kol. A semi-synthetic organism with an expanded genetic alphabet. S. 385–388. Nature [online]. 7. květen 2014. Svazek 509, čís. 7500, s. 385–388. Dostupné online. ISSN 1476-4687. DOI 10.1038/nature13314. PMID 24805238. (anglicky)
- ↑ JOHN, Radek: Vědci stvořili bakterii s novým genetickým kódem. Týden, 12. květen 2014. Dostupné online
- ↑ ZHANG, Yorke; LAMB, Brian M.; FELDMAN, Aaron W.; ZHOU, Anne Xiaozhou; LAVERGNE, Thomas; LI, Lingjun; ROMESBERG, Floyd E. A semisynthetic organism engineered for the stable expansion of the genetic alphabet. Proceedings of the National Academy of Sciences USA (PNAS) [online]. 23. leden 2017 [cit. 2017-01-27]. Online před tiskem. Dostupné online. ISSN 1091-6490. DOI 10.1073/pnas.1616443114. (anglicky)
- ↑ The Scripps Research Institute. Scientists create first stable semisynthetic organism. Phys.org [online]. 23. leden 2017 [cit. 2017-01-27]. Popularizační článek k předchozí referenci. Dostupné online. (anglicky)
- ↑ HOUSER, Pavel. První stabilní polosyntetický organismus. SCIENCEmag.cz [online]. Nitemedia s.r.o., 26. leden 2017 [cit. 2017-01-27]. Dostupné online.
- ↑ GEORGIADIS, Millie M.; SINGH, Isha; KELLETT, Whitney F., HOSHIKA, Shuichi; BENNER, Steven A.; RICHARDS, Nigel G. J. Structural Basis for a Six Nucleotide Genetic Alphabet. S. 6947–6955. Journal of the American Chemical Society [online]. 11. květen 2015. Svazek 137, čís. 21, s. 6947–6955. Dostupné online. ISSN 1520-5126. DOI 10.1021/jacs.5b03482. (anglicky)
- ↑ ZHANG, Liqin; YANG, Zunyi; SEFAH, Kwame, BRADLEY, Kevin M.; HOSHIKA, Shuichi; KIM, Myong-Jung; KIM, Hyo-Joong; ZHU, Guizhi; JIMÉNEZ, Elizabeth; CANSIZ, Sena; TENG, I-Ting; CHAMPANHAC, Carole; McLENDON, Christopher; LIU, Chen; ZHANG, Wen; GERLOFF, Dietlind L.; HUANG, Zhen; TAN, Weihong; BENNER, Steven A. Evolution of Functional Six-Nucleotide DNA. S. 6734–6737. Journal of the American Chemical Society [online]. 12. květen 2015. Svazek 137, čís. 21, s. 6734–6737. Dostupné online. ISSN 1520-5126. DOI 10.1021/jacs.5b02251. (anglicky)
- ↑ kar. Vědci vytvořili „mimozemskou“ DNA, místo čtyř písmen jich má osm. ct24 [online]. Česká televize, 22. únor 2019. Dostupné online.
- ↑ BROWN, Dwayne; LANDAU, Elizabeth. Research creates DNA-like molecule to aid search for alien life. Phys.Org [online]. 21. únor 2019. Dostupné online. (anglicky)
- ↑ HOSHIKA, Shuichi; LEAL, Nicole A.; KIM, Myong-Jung; KIM, Myong-Sang; KARALKAR, Nilesh B.; KIM, Hyo-Joong. Hachimoji DNA and RNA: A genetic system with eight building blocks. Kapitola Supplement: Materials and Methods, s. 1. Science [online]. American Association for the Advancement of Science, 22. únor 2019. Svazek 363, čís. 6429, s. 1. Dostupné online. PDF [1]. ISSN 1095-9203. DOI 10.1126/science.aat0971. PMID 30792304. (anglicky)
Externí odkazy
[editovat | editovat zdroj] Obrázky, zvuky či videa k tématu pár bazí na Wikimedia Commons
Obrázky, zvuky či videa k tématu pár bazí na Wikimedia Commons